Science Score: 57.0%
This score indicates how likely this project is to be science-related based on various indicators:
-
✓CITATION.cff file
Found CITATION.cff file -
✓codemeta.json file
Found codemeta.json file -
✓.zenodo.json file
Found .zenodo.json file -
✓DOI references
Found 4 DOI reference(s) in README -
○Academic publication links
-
○Committers with academic emails
-
○Institutional organization owner
-
○JOSS paper metadata
-
○Scientific vocabulary similarity
Low similarity (3.1%) to scientific vocabulary
Repository
Detect microsaccades
Basic Info
- Host: GitHub
- Owner: robbertmijn
- Language: AGS Script
- Default Branch: main
- Size: 13.8 MB
Statistics
- Stars: 3
- Watchers: 1
- Forks: 2
- Open Issues: 1
- Releases: 2
Metadata Files
README.md
pycrosaccade
Detect microsaccades
Installation
Use pip install
> pip install pycrosaccade
Usage
Use in combination with https://github.com/smathot/python-eyelinkparser/tree/master/eyelinkparser
Preprocessing
``` { .python capture } from pycrosaccade import microsaccades, ms_diagnostics from eyelinkparser import parse, defaulttraceprocessor
Parse data as usual
dm = parse( traceprocessor=defaulttraceprocessor( blinkreconstruct=True, downsample=None, mode = "advanced" ) ) ```
Out:
data/sub_1.asc............................................data/sub_2.asc............................................data/sub_3.asc............................................
Microsaccades
For each phase in the experiment, add 5 columns (saccetlist_phase, saccstlist_phase, saccdurlist_phase, saccdistlist_phase, saccfreq_phase)
``` { .python capture} microsaccades(dm)
print(dm.saccstlist_fixation) ```
Out:
Calculating microsaccades in phase "baseline"
Calculating microsaccades in phase "feedback"
Calculating microsaccades in phase "fixation"
Calculating microsaccades in phase "problem"
Calculating microsaccades in phase "response"
col[[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[1101. nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ 487. nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ 399. 590. nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ 613. nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[1378. nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[1036. nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ 194. nan nan nan nan]
[ nan nan nan nan nan]
[ 785. 898. 1056. 1191. 2360.]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ 884. 1068. nan nan nan]
[ 663. nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ 209. nan nan nan nan]
[1237. nan nan nan nan]
[1268. nan nan nan nan]
[ nan nan nan nan nan]
[ 275. nan nan nan nan]
[1066. 1552. nan nan nan]
[ 143. 779. nan nan nan]
[ 705. nan nan nan nan]
[ nan nan nan nan nan]
[ 569. 792. 1396. nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ 16. nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ 91. 609. 738. 1633. 2209.]
[ 385. nan nan nan nan]
[1558. nan nan nan nan]
[ 474. 715. nan nan nan]
[ 354. 926. nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ 629. 1065. nan nan nan]
[1291. 1590. nan nan nan]
[ 55. 608. 862. 1088. 1940.]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ 478. 1020. 1177. 2420. nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]
[ nan nan nan nan nan]]
Visualisation
{ .python capture }
from matplotlib import pyplot as plt
fig, ax = plt.subplots()
ax.plot(dm.saccfreq_fixation.mean)
fig.savefig('plot.png')
Out:
```
```

To compare the results with different parameters, use ms_diagnostics
{ .python capture }
microsaccades(dm, varname='default')
microsaccades(dm, varname='thres3', msVthres=3)
Out:
Calculating microsaccades in phase "baseline"
Calculating microsaccades in phase "feedback"
Calculating microsaccades in phase "fixation"
Calculating microsaccades in phase "problem"
Calculating microsaccades in phase "response"
Calculating microsaccades in phase "baseline"
Calculating microsaccades in phase "feedback"
Calculating microsaccades in phase "fixation"
Calculating microsaccades in phase "problem"
Calculating microsaccades in phase "response"
{ .python capture }
fig, axs = ms_diagnostics(dm, phase='fixation', varname='default')
fig.savefig('defaults.png')
fig, axs = ms_diagnostics(dm, phase='fixation', varname='thres3')
fig.savefig('thres3.png')
Out:
```
```
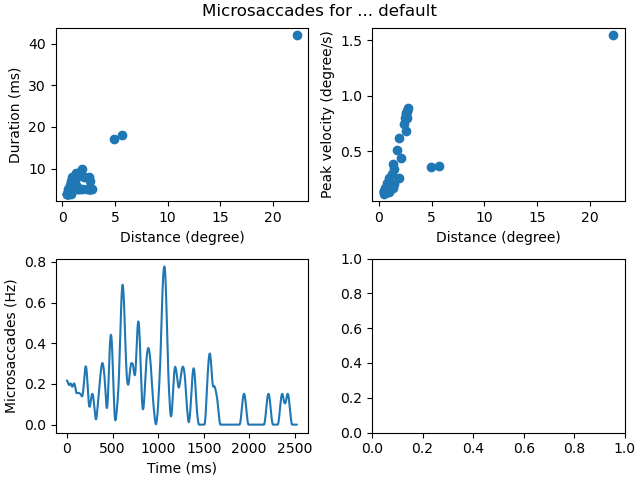
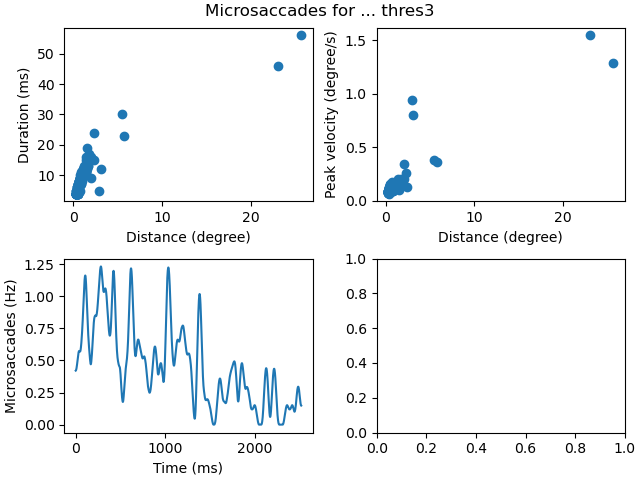
Parameters
TODO (but see functions)
References
- Engbert, R., & Kliegl, R. (2003). Microsaccades uncover the orientation of covert attention. Vision Research, 43(9), 1035–1045. https://doi.org/10.1016/S0042-6989(03)00084-1
- Liu, B., Nobre, A. C., & Ede, F. van. (2021). Functional but not obligatory link between microsaccades and neural modulation by covert spatial attention. bioRxiv. https://doi.org/10.1101/2021.11.10.468033
Owner
- Name: Robbert van der Mijn
- Login: robbertmijn
- Kind: user
- Website: robbertmijn.nl
- Twitter: robbertmijn
- Repositories: 4
- Profile: https://github.com/robbertmijn
Citation (CITATION.cff)
# This CITATION.cff file was generated with cffinit.
# Visit https://bit.ly/cffinit to generate yours today!
cff-version: 1.2.0
title: pycrosaccade
message: >-
If you use this software, please cite it using these
metadata.
type: software
authors:
- family-names: Mijn
given-names: Robbert
orcid: 'https://orcid.org/0000-0002-5312-2613'
name-particle: van der
email: robbertmijn@gmail.com
repository-code: 'https://github.com/robbertmijn/pycrosaccade'
abstract: Detect microsaccades
version: 0.5.0
date-released: '2023-02-01'
GitHub Events
Total
- Watch event: 1
Last Year
- Watch event: 1
Committers
Last synced: about 3 years ago
All Time
- Total Commits: 30
- Total Committers: 1
- Avg Commits per committer: 30.0
- Development Distribution Score (DDS): 0.0
Top Committers
| Name | Commits | |
|---|---|---|
| robbertmijn | r****n@g****m | 30 |
Issues and Pull Requests
Last synced: 8 months ago
All Time
- Total issues: 2
- Total pull requests: 2
- Average time to close issues: 1 day
- Average time to close pull requests: 4 days
- Total issue authors: 2
- Total pull request authors: 1
- Average comments per issue: 0.5
- Average comments per pull request: 0.5
- Merged pull requests: 1
- Bot issues: 0
- Bot pull requests: 0
Past Year
- Issues: 1
- Pull requests: 0
- Average time to close issues: N/A
- Average time to close pull requests: N/A
- Issue authors: 1
- Pull request authors: 0
- Average comments per issue: 0.0
- Average comments per pull request: 0
- Merged pull requests: 0
- Bot issues: 0
- Bot pull requests: 0
Top Authors
Issue Authors
- olafdimigen (1)
- smathot (1)
Pull Request Authors
- IvoryYChen (2)
Top Labels
Issue Labels
Pull Request Labels
Packages
- Total packages: 1
-
Total downloads:
- pypi 52 last-month
- Total dependent packages: 0
- Total dependent repositories: 0
- Total versions: 12
- Total maintainers: 1
pypi.org: pycrosaccade
Detect microsaccades
- Documentation: https://github.com/robbertmijn/pycrosaccade
- License: MIT License
-
Latest release: 0.5.0
published over 2 years ago
Rankings
Maintainers (1)
Dependencies
- numpy *
- python-datamatrix *